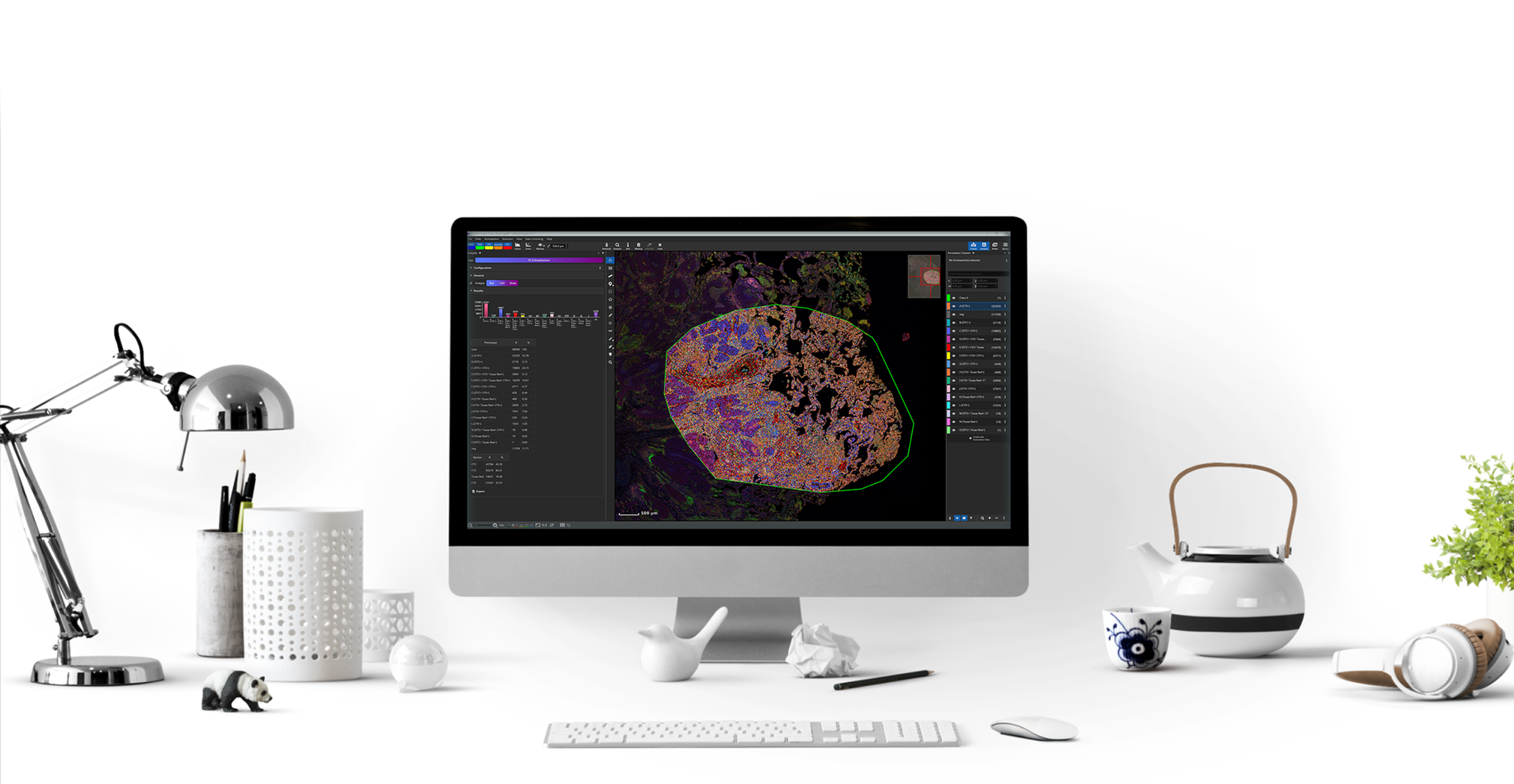
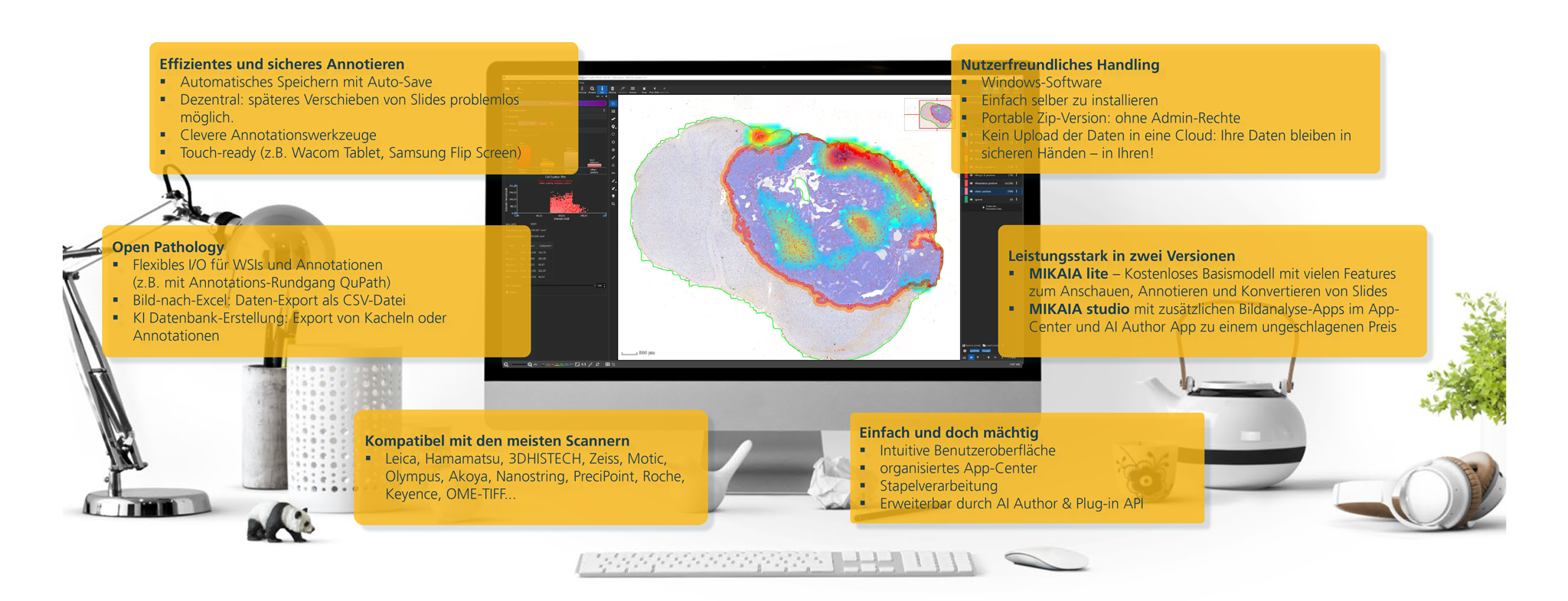
MIKAIA1 ist die ideale Software für die präklinische und klinische Forschung – genau abgestimmt auf die Anforderungen und spezifischen Forschungsfragen der Histopathologie:
- Annotieren von Whole-Slide-Images, in Hellfeld oder Fluoreszenz
- Effizientes Analysieren von mehr Daten – für objektive und quantitative Ergebnisse
- Bild-nach-Excel-Funktionalität für die quantitative Pathologie
- "Off the Shelf"-Apps für Standard-Use-Cases sowie flexible Erweiterungsoptionen für individuelle Anwendungsfälle
- Ideal für Standard-Pathologie (H&E), Immunohistochemie sowie Proteomics/Spatial Biology.